脑影像数据分析涉及细节繁多、琐碎问题多,短时间内难以彻底掌握。基于脑海科技多年的服务经验,我们深感有必要系统梳理相关问题。为了更好地服务广大研究者,我们将把科研中合作者以及研究生提出的真实问题,以“一问一答”的形式整理出来,定期分享。希望能为您的研究提供一点参考。
BrainNet viewer可以用来制作什么样的脑图,如何选择合适的呈现方式?
BrainNet Viewer 是一款常用的脑网络可视化工具,支持多种脑图类型。根据研究需求不同,可选择以下几种呈现方式:
| 图示类型 | 适用场景 |
| 皮层图 | 展示全脑皮层的统计差异图(如ALFF、ReHo、GMV组间差异) |
| ROI图 | 展示感兴趣脑区或网络的解剖位置 |
| 球形图 | 展示节点(脑区)的空间分布,常用于坐标可视化 |
| 球棍图 | 展示脑网络节点之间的连接关系(功能/结构连接) |
用途:软件可将三维NIFTI统计文件(如 ALFF、ReHo、GMV值组间差异)直接渲染在大脑皮层,通过的不同颜色以映射脑区的差异方向与强度,直观展示全脑皮层的激活 / 减弱、升高 / 降低区域。使用场景举例:基于体素的统计分析结果(ALFF、fALFF、ReHo、DC、基于种子点的功能连接、基于种子点的格兰杰因果分析等)1)输入文件:在Surface files中选择底板文件,Mapping file中选择要呈现的NIFTI文件,如指标差异结果文件(例如T2_G1MG2_grfp01_05_TT_CSauto_CC.nii)。2)参数调整:在Volume中选择Volume to surface后可根据下图参数说明进行调整。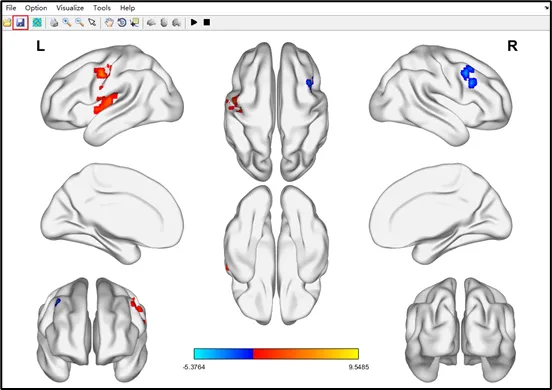
用途:展示分析中的感兴趣脑区或网络,使用半透明底板和不同颜色ROI,清晰呈现ROI的解剖位置。1)输入文件:在Surface files中选择底板文件,Mapping file中选择要呈现的脑区或网络文件(NIFTI格式)。2)底板透明度:在Surface中调节底板透明度,常用数值为0.3。3)参数调整:在Volume中选择ROI drawing后可根据下图参数说明进行调整。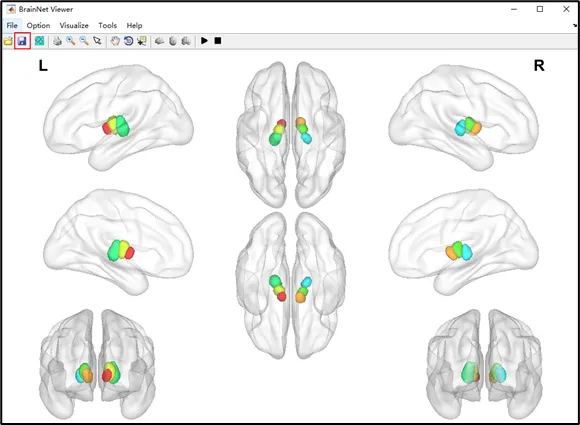
用途:仅展示节点(小球)的空间分布图,适用于已知脑区坐标的情况。通过小球颜色、大小区分脑区所属网络或效应量大小。1)Node文件制作:新建一个记事本,格式内容为[x y z 颜色 大小 名称]。一行为一个小球,x y z为小球的坐标,颜色可以用于区分不同的脑区或不同的网络,大小可以用于区分不同的效应量或者体素数量,名称后续可选择性的呈现在球图中。制作好后可将该文档修改为“.node”格式;2)输入文件:在Surface files中选择底板文件,Data file (node)中选择要呈现的node文件。3)底板透明度:在Surface中调节底板透明度,常用数值为0.3。4)参数调整:在Node中根据下图参数说明进行调整。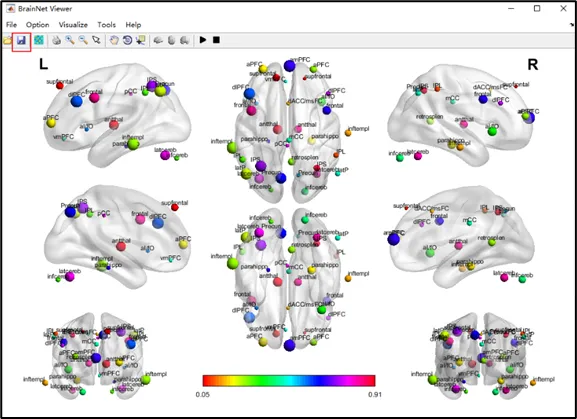
用途:展示脑网络节点之间的连接关系(功能/结构连接),由“球”(节点)和“棍”(连接线)组成,适合用于脑网络可视化。1)Node文件制作:新建一个记事本,格式内容为[x y z 颜色 大小 名称]。一行为一个小球,x y z为小球的坐标,颜色可以用于区分不同的脑区或不同的网络,大小可以用于区分不同的效应量或者体素数量,名称后续可选择性的呈现在球图中。制作好后可将该文档保存为“.node”格式。2)Edge文件制作:新建一个记事本,格式为n*n的矩阵。如ROI的数量为3,需构建3*3的矩阵。矩阵坐标的数值代表两个脑区之间的连接情况,例如,坐标位置 (1, 2) 的数值表示第 1 行脑区与第 2 行脑区的连接情况。如果脑区间有连接,可在坐标位置填入“1”或差异t值;如果两者之间没有连接的结果,可在坐标位置填入“0”;制作好后可将该文档保存为“.edge”格式。3)输入文件:在Surface files中选择底板文件,Data file (node)中选择要呈现的node文件,Data file (edge)中选择要呈现的edge文件。4)底板透明度:在Surface中调节底板透明度,常用数值为0.3。5)Node参数调整:在Node中根据下图参数说明进行调整。6)Edge参数调整:在Edge中根据下图参数说明进行调整。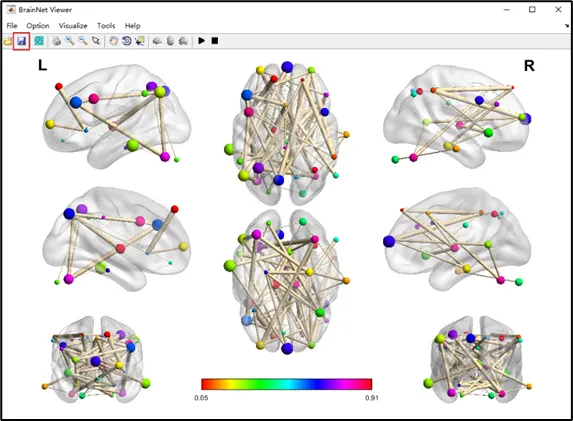
本期介绍了 BrainNet Viewer 常用的四种脑图类型及其操作流程。根据研究目的选择合适的可视化方式,可以更直观地展示脑影像结果。
欢迎关注脑海科技云平台。平台提供从原始数据到统计结果的全流程自动化处理,以及项目管理、质量控制、团队协作等一站式服务,为多中心、大样本研究提供坚实的数据基础,助力您的科研工作高效推进。
扫描下方二维码/点击链接,预约平台演示!扫码添加顾问,备注“平台演示预约”
19906719439(微信同号)